METODO PARA LA DETECCION ELECTROQUIMICA DE SECUENCIAS DE ACIDOS NUCLEICOS.
Método para la detección electroquímica de secuencias de ácidos nucleicos.
Es objeto de la presente invención un nuevo compuesto derivado de rutenio, de fórmula (I), denominado complejo de pentamin rutenio [3-(2-fenantren-9-il-vinil)piridina], así como su empleo como indicador electroquímico de hibridación en un método para la detección de hibridación entre secuencias de ácidos nucleicos, para la cuantificación de dichas secuencias, así como la detección de la presencia de una base desapareada y su posición dentro de una secuencia de ácido nucleico
Tipo: Patente de Invención. Resumen de patente/invención. Número de Solicitud: P200701446.
Solicitante: UNIVERSIDAD AUTONOMA DE MADRID.
Nacionalidad solicitante: España.
Provincia: MADRID.
Inventor/es: LORENZO ABAD,ENCARNACION, PARIENTE ALONSO,FELIX, REVENGA PARRA,MONICA, GARCIA MENDIOLA,TANIA.
Fecha de Solicitud: 25 de Mayo de 2007.
Fecha de Publicación: .
Fecha de Concesión: 29 de Octubre de 2009.
Clasificación Internacional de Patentes:
- C07D213/90 QUIMICA; METALURGIA. › C07 QUIMICA ORGANICA. › C07D COMPUESTOS HETEROCICLICOS (Compuestos macromoleculares C08). › C07D 213/00 Compuestos heterocíclicos que contienen ciclos de seis miembros, no condensados con otros ciclos, con un átomo de nitrógeno como el único heteroátomo del ciclo y tres o más enlaces dobles entre miembros cíclicos o entre miembros cíclicos y miembros no cíclicos. › teniendo más de tres enlaces dobles entre miembros cíclicos o entre miembros cíclicos y miembros no cíclicos.
- C12Q1/68 C […] › C12 BIOQUIMICA; CERVEZA; BEBIDAS ALCOHOLICAS; VINO; VINAGRE; MICROBIOLOGIA; ENZIMOLOGIA; TECNICAS DE MUTACION O DE GENETICA. › C12Q PROCESOS DE MEDIDA, INVESTIGACION O ANALISIS EN LOS QUE INTERVIENEN ENZIMAS, ÁCIDOS NUCLEICOS O MICROORGANISMOS (ensayos inmunológicos G01N 33/53 ); COMPOSICIONES O PAPELES REACTIVOS PARA ESTE FIN; PROCESOS PARA PREPARAR ESTAS COMPOSICIONES; PROCESOS DE CONTROL SENSIBLES A LAS CONDICIONES DEL MEDIO EN LOS PROCESOS MICROBIOLOGICOS O ENZIMOLOGICOS. › C12Q 1/00 Procesos de medida, investigación o análisis en los que intervienen enzimas, ácidos nucleicos o microorganismos (aparatos de medida, investigación o análisis con medios de medida o detección de las condiciones del medio, p. ej. contadores de colonias, C12M 1/34 ); Composiciones para este fin; Procesos para preparar estas composiciones. › en los que intervienen ácidos nucleicos.
- G01N33/53 FISICA. › G01 METROLOGIA; ENSAYOS. › G01N INVESTIGACION O ANALISIS DE MATERIALES POR DETERMINACION DE SUS PROPIEDADES QUIMICAS O FISICAS (procedimientos de medida, de investigación o de análisis diferentes de los ensayos inmunológicos, en los que intervienen enzimas o microorganismos C12M, C12Q). › G01N 33/00 Investigación o análisis de materiales por métodos específicos no cubiertos por los grupos G01N 1/00 - G01N 31/00. › Ensayos inmunológicos; Ensayos en los que interviene la formación de uniones bioespecíficas; Materiales a este efecto.
Clasificación PCT:
- C07D213/90 C07D 213/00 […] › teniendo más de tres enlaces dobles entre miembros cíclicos o entre miembros cíclicos y miembros no cíclicos.
- C12Q1/68 C12Q 1/00 […] › en los que intervienen ácidos nucleicos.
- G01N33/53 G01N 33/00 […] › Ensayos inmunológicos; Ensayos en los que interviene la formación de uniones bioespecíficas; Materiales a este efecto.
Fragmento de la descripción:
Método para la detección electroquímica de secuencias de ácidos nucleicos.
Campo de la invención
La presente invención se refiere a un método para la detección de la hibridación de ácidos nucleicos mediante métodos electroquímicos. Más concretamente, la presente invención se refiere a un método para la detección de una secuencia de ADN determinada, la presencia de un desapareamiento en dicha secuencia, así como su posición, basado en el empleo de un compuesto derivado de rutenio de fórmula general (I) como indicador de hibridación en biosensores electroquímicos.
Antecedentes de la invención
El diagnóstico molecular basado en el análisis de secuencias cortas de ADN ofrece métodos sensibles y cuantitativos para la detección temprana de enfermedades infecciosas producidas por patógenos (Garg, S. K. et al. Clin. Lab. Anal. 2003, 17(5), 155-163; Vernet, G. Virus Res. 2002, 82(1-2), 65-71).
La hibridación del ADN es el proceso más común para analizar y detectar un gen particular o un segmento de un ácido nucleico. Entre los métodos basados en hibridación se encuentran aquellos basados en resonancias de plasmón superficial (Mullet, W. M. et al. Methods 2000, 22, 77-91; Sawata, S. et al. Biosens. Bioelectron. 1999, 14, 397-404; Livache, T. et al Synth. Met. 2001, 121, 1443-1444; Wood, S. J. Microchem. J. 1993, 47, 330-337), fluorescencia (Piunno, P. A. E. et al. Anal. Chim. Acta, 1994, 288, 205-214; Fodor, S. et al Science, 1991, 251, 767-773), gravimetría (Okahata, Y. et al. Am. Chem. Soc. 1992, 114, 8299-8300; Minnuni, M. et al. Anal Chim. Acta, 2003, 481, 55-64) o marcaje con radioisótopos (Séller, G. H. et al DNA Probes, 2nd ed. Stockton Press: New York, 1993; pp 149-213). El método más empleado es el uso de fragmentos de ADN o ARN marcados radiactivamente, conocidos como sondas. De hecho, esta metodología es la base de la amplificación controlada de ADN conocida como PCR (Reacción en Cadena de la Polimerasa) que se utiliza para la clonación y secuenciación de ADN.
Entre los métodos basados en hibridación, los biosensores de ADN presentan ventajas en comparación con los métodos citados. Una de las ventajas de estos métodos es la posibilidad de desarrollar dispositivos portátiles simples para este tipo de diagnóstico. Además, el acoplamiento entre estos biosensores de ADN y las técnicas de amplificación por PCR pueden proporcionar una gran sensibilidad para la detección de secuencias de ácidos nucleicos (Meric, B. et al. Talanta 2002, 56(5), 837-846). El uso de oligonucleótidos marcados con fluorescencia inmovilizados sobre una superficie ha permitido el desarrollo de arrays de ADN de alta densidad para el análisis de secuencias específicas de ADN y de expresión génica. Sin embargo, estos métodos requieren el marcaje del ADN diana (Berre, V. L. et al. Nucleic Acids Res. 2003, 31, e88; Dolan, P. L. et al. Nucleic Acids Res. 2001, 29, 107).
Como el ADN posee unas bandas nucleicas electroactivas, también se han desarrollado sistemas electroquímicos de detección sacando partido de esta propiedad para detectar directamente el ADN hibridado, sin tener que hacer intervenir un marcador (Park, S. et al. Science, 2002, 295, 1503-1506; Drummond, T.G. et al. Nat. Biotech., 2003, 21, 1192-1199). De manera general, el ADN se inmoviliza sobre un electrodo, y la diferencia de corriente eléctrica medida antes y después de la hibridación está relacionada con la cantidad de ADN fijado sobre el electrodo (WO93/20230). Sin embargo, esta detección directa sin marcador no es muy sensible.
Con la finalidad de mejorar la sensibilidad, se han desarrollado diferentes aproximaciones que emplean una molécula sonda electroactiva o un marcador electroactivo. Así, Palanti et al. (1996, Analytical Letters, 29, pp. 2309-31) describen diferentes compuestos electroactivos, que pueden asociarse con el ADN y así ser detectados por oxidación-reducción aplicando un potencial al electrodo. Así, se han empleado complejos de metales de transición, antibióticos, colorantes de acridina o de benzamida y otros agentes intercalantes del ADN.
Como estas sondas o marcadores electroactivos poseen mejores propiedades de oxidorreducción que el ADN, su utilización permite obtener una relación señal/ruido superior y una mejor sensibilidad.
Se han empleado también como indicadores electroquímicos compuestos derivados del salophen (Revenga Parra, M. et al. "Comprehensive study of the interactions between DNA and new Schiff base ligands containing quinone functional groups" Biosensors and Bioelectronics. Volumen: 22; Págs 2675-2681) y complejos de Osmio (Del Pozo, M. V. et al. Anal. Chem. 2005a.77 (8), 2550-2557). En el documento CA02524263 se emplean complejos de rutenio como indicadores de hibridación, que se incorporan a la doble cadena a circuito abierto.
Ahora, los autores de la presente invención han desarrollado un método que permite mejorar la sensibilidad de la detección electroquímica de secuencias de ácidos nucleicos gracias al empleo de un nuevo complejo de rutenio, preparado "in situ", denominado complejo de pentamin rutenio [3-(2-fenantren-9-il-vinil)piridina] (referido como RuL), como indicador de hibridación en biosensores electroquímicos.
El complejo RuL, formado por la unión entre el complejo pentamin rutenio (Ru) y el ligando 3-(2-fenantren-9-il-vinil)piridina (L), es totalmente novedoso, así como su empleo con esta finalidad.
La alta sensibilidad y especificidad conseguida con el método desarrollado permite detectar y cuantificar, sin necesidad de ningún tipo de marcaje, no sólo una secuencia determinada de ácido nucleico, sino también un único desapareamiento en una base de dicha secuencia, así como su posición dentro de la secuencia específica del ácido nucleico, suponiendo además un sistema de detección mucho más rápido y económico que los clásicos PCR.
Breve descripción de las figuras
Figura 1. a) Voltamogramas diferenciales de pulsos (DPVs) de RuL acumulado en un electrodo de oro modificado con SEQ ID Nº 1 antes (2) y después de la hibridación con la cadena complementaria (SEQ ID NO 2) (1) y no complementaria (SEQ ID Nº 3) (3). b) Ampliación del DPVs de -0,6 a 0 V del barrido de potencial.
Figura 2. Voltamogramas diferenciales de pulsos (DPVs) de RuL acumulado en un electrodo de oro modificado con (SEQ ID Nº 1): después de la hibridación con una secuencia desapareada en una base en el medio (SEQ ID Nº 4) (2) después de la hibridación con una secuencia desapareada (próxima al extremo 5' de la secuencia, (SEQ ID Nº 5), (3) después de la hibridación con una secuencia desapareada próxima al extremo 3' de la secuencia, (SEQ ID Nº 6), (4) y después de la hibridación con una secuencia no complementaria (SEQ ID Nº 3) (1).
Objeto de la invención
Es objeto de la presente invención un nuevo compuesto derivado de rutenio de fórmula (I), denominado complejo de pentamin rutenio [3-(2-fenantren-9-il-vinil)piridina].
Es también objeto de la invención un método para la detección de hibridación entre una sonda y una secuencia diana de ácido nucleico basado en el empleo de dicho complejo de fórmula I como indicador de la hibridación.
Finalmente, es objeto de la presente invención el empleo del compuesto derivado de rutenio de fórmula (I) como indicador electroquímico de hibridación entre secuencias de ácidos nucleicos.
Descripción detallada de la invención
Los autores de la presente invención han obtenido, tras un importante trabajo de investigación, un nuevo compuesto derivado de rutenio cuya estructura permite su empleo como indicador del proceso de hibridación entre secuencias de ácidos nucleicos en biosensores electroquímicos para la detección del desapareamiento de una sola base, así como su posición dentro de la secuencia.
Así, un aspecto principal de la invención se refiere a un nuevo compuesto derivado de rutenio de fórmula (I):
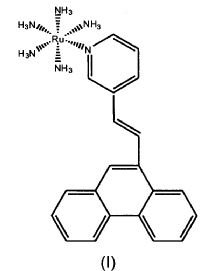
Este nuevo complejo, denominado pentamin rutenio [3-(2-fenantren-9-il-vinil)piridina] (referido como RuL), preparado in situ, presenta, gracias a su estructura, una doble función. Por un lado, la estructura planar de los grupos aromáticos del ligando 3-(2-fenantren-9-il-vinil) piridina (L) confiere un carácter intercalativo al complejo y le permite, por tanto, unirse a ácidos nucleicos de doble...
Reivindicaciones:
1. Compuesto derivado de rutenio de fórmula (I):
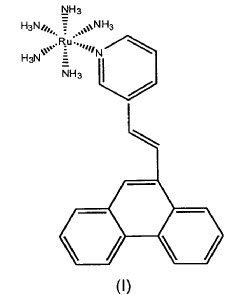
2. Método para la detección de hibridación entre una sonda y una secuencia diana de ácido nucleico caracterizado porque comprende las siguientes etapas:
donde la detección de hibridación permite la detección de una secuencia de ácido nucleico, la cuantificación de secuencias de ácido nucleico, la detección de una base desapareada en una secuencia de ácido nucleico o la detección de la posición de dicho base desapareada.
3. Método según la reivindicación 2, caracterizado porque el ácido nucleico de la sonda y la secuencia diana es ADN.
4. Método según la reivindicación 3, caracterizado porque el electrodo empleado es de oro.
5. Método, según la reivindicación 4, caracterizado porque los barridos cíclicos de potencial se aplican 200 veces, entre -0.5 y 0.1 V.
6. Método, según la reivindicación 4, caracterizado porque la detección electroquímica se lleva a cabo por voltamperametría diferencial de pulsos a una velocidad de barrido de 10 Mv/s, una amplitud de pulso de 50 mV y una anchura de pulso de 0.2 s.
7. Empleo del compuesto, según la reivindicación 1, como indicador electroquímico de hibridación entre secuencias de ácidos nucleicos.
8. Empleo del compuesto, según la reivindicación 7, para la detección de una secuencia de ácido nucleico.
9. Empleo del compuesto, según la reivindicación 7, para la cuantificación de secuencias de ácidos nucleicos.
10. Empleo del compuesto, según la reivindicación 7, para la detección de una base desapareada en una secuencia de ácido nucleico.
11. Empleo del compuesto, según la reivindicación 7, para la detección de la posición de una base desapareada en una secuencia de ácido nucleico.
12. Empleo del compuesto, según cualquiera de las reivindicaciones 7-11, donde el ácido nucleico es ADN.
Patentes similares o relacionadas:
Método para analizar ácido nucleico molde, método para analizar sustancia objetivo, kit de análisis para ácido nucleico molde o sustancia objetivo y analizador para ácido nucleico molde o sustancia objetivo, del 29 de Julio de 2020, de Kabushiki Kaisha DNAFORM: Un método para analizar un ácido nucleico molde, que comprende las etapas de: fraccionar una muestra que comprende un ácido nucleico molde […]
MÉTODOS PARA EL DIAGNÓSTICO DE ENFERMOS ATÓPICOS SENSIBLES A COMPONENTES ALERGÉNICOS DEL POLEN DE OLEA EUROPAEA (OLIVO), del 23 de Julio de 2020, de SERVICIO ANDALUZ DE SALUD: Biomarcadores y método para el diagnostico, estratificación, seguimiento y pronostico de la evolución de la enfermedad alérgica a polen del olivo, kit […]
Detección de interacciones proteína a proteína, del 15 de Julio de 2020, de THE GOVERNING COUNCIL OF THE UNIVERSITY OF TORONTO: Un método para medir cuantitativamente la fuerza y la afinidad de una interacción entre una primera proteína de membrana o parte de la misma y una […]
Secuenciación dirigida y filtrado de UID, del 15 de Julio de 2020, de F. HOFFMANN-LA ROCHE AG: Un procedimiento para generar una biblioteca de polinucleótidos que comprende: (a) generar una primera secuencia del complemento (CS) de un polinucleótido diana a partir […]
Métodos para la recopilación, estabilización y conservación de muestras, del 8 de Julio de 2020, de Drawbridge Health, Inc: Un método para estabilizar uno o más componentes biológicos de una muestra biológica de un sujeto, comprendiendo el método obtener un […]
Evento de maíz DP-004114-3 y métodos para la detección del mismo, del 1 de Julio de 2020, de PIONEER HI-BRED INTERNATIONAL, INC.: Un amplicón que consiste en la secuencia de ácido nucleico de la SEQ ID NO: 32 o el complemento de longitud completa del mismo.
Composiciones para modular la expresión de SOD-1, del 24 de Junio de 2020, de Biogen MA Inc: Un compuesto antisentido según la siguiente fórmula: mCes Aeo Ges Geo Aes Tds Ads mCds Ads Tds Tds Tds mCds Tds Ads mCeo Aes Geo mCes Te (secuencia […]
Aislamiento de ácidos nucleicos, del 24 de Junio de 2020, de REVOLUGEN LIMITED: Un método de aislamiento de ácidos nucleicos que comprenden ADN de material biológico, comprendiendo el método las etapas que consisten en: (i) efectuar un lisado […]