Moduladores de la actividad ubiquitinasa Itch.
Un método in vitro de modulación de la apoptosis en una célula,
que comprende la etapa de disminuir o alterar de otra forma la actividad funcional del polipéptido de ligasa de ubiquitina E3 Itch o el ácido nucleico que lo codifica, usando ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch.
Tipo: Patente Internacional (Tratado de Cooperación de Patentes). Resumen de patente/invención. Número de Solicitud: PCT/GB2006/000181.
Solicitante: Ryboquin Company Limited.
Inventor/es: ROSSI, MARIO, MELINO,GENNARO, SALOMONI,PAOLO.
Fecha de Publicación: .
Clasificación Internacional de Patentes:
- A61P17/00 NECESIDADES CORRIENTES DE LA VIDA. › A61 CIENCIAS MEDICAS O VETERINARIAS; HIGIENE. › A61P ACTIVIDAD TERAPEUTICA ESPECIFICA DE COMPUESTOS QUIMICOS O DE PREPARACIONES MEDICINALES. › Medicamentos para el tratamiento de problemas dermatológicos.
- A61P35/00 A61P […] › Agentes antineoplásicos.
- A61P37/00 A61P […] › Medicamentos para el tratamiento de problemas inmunológicos o alérgicos.
- G01N33/573 FISICA. › G01 METROLOGIA; ENSAYOS. › G01N INVESTIGACION O ANALISIS DE MATERIALES POR DETERMINACION DE SUS PROPIEDADES QUIMICAS O FISICAS (procedimientos de medida, de investigación o de análisis diferentes de los ensayos inmunológicos, en los que intervienen enzimas o microorganismos C12M, C12Q). › G01N 33/00 Investigación o análisis de materiales por métodos específicos no cubiertos por los grupos G01N 1/00 - G01N 31/00. › para enzimas o isoenzimas.
- G01N33/574 G01N 33/00 […] › para el cáncer.
PDF original: ES-2524246_T3.pdf



Fragmento de la descripción:
Moduladores de la actividad ubiquitinasa Itch
Resumen de la invención La presente invención se refiere a la identificación de nuevas dianas de fármacos para terapias de trastornos que incluyen el cáncer. En particular, la presente invención se refiere a la inhibición de la ligasa de ubiquitina E3, Itch, como medio para tratar trastornos. Además, la presente invención se refiere a la regulación de la estabilidad de p63 y p73 en células. En particular, la invención se refiere a la modulación de la regulación de la estabilidad de p63 y p73 en células mediante la modulación de la expresión o actividad de Itch. Además, la invención se refiere al uso de Itch como una diana para el desarrollo de agentes capaces de modular la estabilidad de p63 o p73, y en especial agentes capaces de modular la interacción de Itch y p63 o p73. Dichos agentes pueden ser útiles en aplicaciones terapéuticas incluyendo el tratamiento del cáncer y la modulación de la diferenciación de la piel.
Antecedentes de la invención Aunque la comprensión de los mecanismos y el posible tratamiento del cáncer han aumentado a lo largo de los últimos años, el cáncer sigue siendo una causa principal de muerte en todo el mundo desarrollado. Procedimientos no específicos para el tratamiento del cáncer, tales como la cirugía, radioterapia y quimioterapia generalizada, han tenido éxito en el tratamiento de algunos cánceres sólidos en la circulación y de crecimiento lento. Sin embargo, muchos tipos de cánceres son, en general, muy resistentes a los tratamientos convencionales. Por consiguiente, son necesarias terapias para el cáncer adicionales y más eficaces.
El desarrollo de nuevas terapias depende de la identificación de dianas adecuadas para la actividad del fármaco.
El gen supresor de tumores p53 induce la detención del ciclo celular y promueve la apoptosis previniendo así la transformación de células. La inactivación del gen supresor de tumores p53 es el defecto genético más común que afecta a más de la mitad de todos los tumores humanos. La proteína p53 es estabilizada en respuesta al estrés genotóxico, cambios metabólicos y otros sucesos potencialmente peligrosos que pueden producir la transformación de células.
p63 y p73 son miembros de la familia p53 de factores de transcripción y se ha mostrado que actúan en una ruta paralela a la de p53, siendo regulados por aumento en respuesta al daño al ADN e induciendo detención del crecimiento y apoptosis en una ruta independiente de p53. La regulación y función de p63 y p73 se revisa en Melino et al. 2003. Ambos inducen la detención del ciclo celular y apoptosis y se ha mostrado recientemente que actúan como supresores tumorales in vivo (Flores et al., 2005) .
La importancia de p63 y p73 en la supresión tumoral se demuestra al encontrar que la alteración de p63 y p73 en células p53-/- aumenta su capacidad de transformación. Recientemente, se ha mostrado que las mutaciones de p53 específicas encontradas normalmente en cánceres tales como el síndrome de Li Fraumeni, conducen a la inactivación funcional de p73 y p63, y por lo tanto la inactivación de p63 y p73 es importante para la carcinogénesis in vivo (Lang et al., 2004; Olive et al., 2004) .
Tanto p63 como p73, al igual que p53, tienen una estructura modular (figura 1A) (Kaghad, 1997) . Comparten un grado alto de homología de la secuencia con p53 y se pueden unir a elementos sensibles a p53 que activan la transcripción de genes diana de p53, tales como los que inducen la detención del ciclo celular y promueven la apoptosis (Catani, 2002; De Laurenzi, 1998; De Laurenzi, 2000) .
Sin embargo, a diferencia de p53, p73 y p63 son expresados como isoformas diferentes (Kaghad, 1997; Ueda, 1999) algunas de las cuales carecen del dominio de transactivación y se cree que actúan como proteínas negativas dominantes (Melino, G et al.) . La mayor parte de la variación generada por el corte y empalme alternativo se produce en el extremo 3’, en una parte de la secuencia que no tiene un equivalente en p53. La existencia de estas isoformas variantes ha hecho difícil determinar la importancia de p63 y p73 en la supresión tumoral. Sin embargo, un trabajo reciente usando ratones mutantes para p63/p73 ha demostrado claramente que ambas proteínas tienen funciones supresoras de tumores independientes de p53. Además, los ratones mutantes para p63 y p73 tienen predisposición a tumores epiteliales agresivos comunes en seres humanos (p. ej., adenocarcinomas de pulmón y mamario) , a diferencia de los ratones mutantes para p53, que desarrollan principalmente linfomas tímicos y sarcomas (Flores et al., 2005) .
Al menos seis proteínas diferentes p73 (de α a η) son generadas (De Laurenzi, 1999; De Laurenzi, 1998; Ueda, 1999) mientras que al menos tres proteínas diferentes p63 son generadas como formas isómeras de corte y empalme alternativo C-terminal. Además, tanto los genes de p63 como p73 explotan un promotor alternativo y un exón extra (exón 3') para generar isoformas truncadas N-terminales (ΔNp63 y ΔNp73) . Estas variantes carecen del dominio de transactivación y actúan como “negativos dominantes”, bloqueando la función de proteínas de longitud completa p53, p63 o p73 (Grob, 2001; Sayan et al., 2004; Yang, 2000) . Los niveles relativos de las isoformas TA y ΔN determinan el destino celular, produciendo la detención del crecimiento y muerte o la proliferación no controlada.
Los niveles en equilibrio de proteína TAp73 son regulados por aumento en respuesta al daño al ADN en una forma distinta de p53 (Agami, 1999; Gong, 1999; Yuan, 1999) , mientras que ΔNp73 es degenerada rápidamente (Maisse et al., 2004) . La expresión de ΔNp63 es reducida de forma transcripcional por p53 sugiriendo que no inhibe la actividad de supresión tumoral de p53 y TAp73 de la misma forma. Estas observaciones sugieren una función diferencial importante para estos isómeros en la carcinogénesis (Melino, 2002; Melino et al., 2003; Stiewe, 2002; Zaika, 2002) .
La función de p63 y p73 en el ciclo celular y apoptosis sugiere que su modificación puede contribuir a potenciar la muerte celular en tumores. Además, varias mutaciones en p63 se asocian con síndromes epidérmicos genéticos mientras que el exceso de expresión de p73 es suficiente para producir la diferenciación neuronal. Por consiguiente, la modificación de la estabilidad de p63 o p73 puede ser una estrategia terapéutica en el tratamiento del cáncer y/o trastornos de desarrollo.
Aunque la ubiquitinación y degradación dependiente de proteosoma de p53 es regulada por su diana transcripcional MDM2, la regulación de la degradación de las proteínas p73 y p63 es controlada por distintas ligasas E3. Hasta ahora, se conoce muy poco sobre los mecanismos moleculares que subyacen en la regulación de los niveles en equilibrio de las proteínas p63 y p73 y su modulación como una posible estrategia terapéutica no se ha explorado completamente. Aunque algunos procedimientos han buscado el uso de inhibidores de proteosoma para inhibir la degradación de proteínas de la familia p53 e inducir así la apoptosis, en ensayos clínicos se ha encontrado que estos inhibidores tienen muy poca especificidad y conducen a la regulación por aumento de un gran número de proteínas. Además, aunque se han dirigido una serie de estrategias terapéuticas a p53, más de 50% de los tumores son deficientes en p53. Por consiguiente, son necesarios tratamientos terapéuticos que puedan dirigirse a rutas independientes de p53.
El documento D18 (WO99/40201) describe una proteína ligasa de ubiquitina E3 humana. Se describe una región estructural que codifica el polipéptido así como la secuencia de restos de aminoácidos de la proteína ligasa de ubiquitina humana. Se proporcionan métodos para identificar compuestos que modulan la actividad biológica y por lo tanto regulan la fisiología celular y tisular.
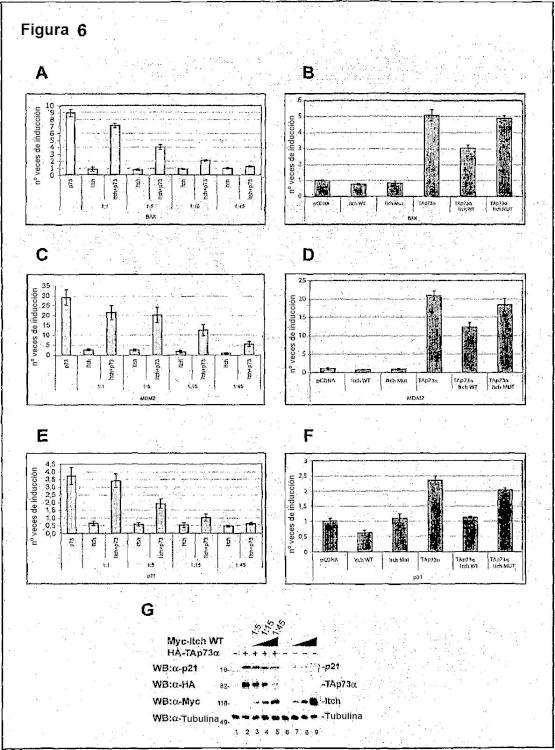
Sumario de la invención La presente invención identifica que una modulación de la actividad de Itch puede proporcionar una respuesta celular importante para la terapia de diferentes trastornos. En particular, la presente invención demuestra que una inhibición de la actividad de Itch regula la apoptosis en una célula.
Se exponen aspectos de la invención en las reivindicaciones independientes adjuntas.
En una realización, se proporciona un método de modulación de la apoptosis en una célula, que comprende la etapa de disminuir o alterar de otra forma la actividad funcional del polipéptido Itch o el ácido nucleico que lo codifica. Los cambios en la actividad de Itch producen una estabilidad alterada en las proteínas p63 y p73, así como su actividad, tal como por ejemplo,... [Seguir leyendo]
Reivindicaciones:
1. Un método in vitro de modulación de la apoptosis en una célula, que comprende la etapa de disminuir o alterar de otra forma la actividad funcional del polipéptido de ligasa de ubiquitina E3 Itch o el ácido nucleico que lo codifica, usando ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch.
2. Un método in vitro según la reivindicación 1, en donde la actividad funcional alterada de la ligasa de ubiquitina E3 Itch es la inhibición de la ligasa de ubiquitina E3 Itch.
3. Un método in vitro para sensibilizar células frente a agentes que dañan al ADN mediante la inhibición de la actividad de la ligasa de ubiquitina E3 Itch, usando ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch.
4. Un método in vitro para modular la estabilidad de p63 o p73 en una célula, que comprende modular la actividad
5. Un método in vitro de aumento de la sensibilidad de una célula tumoral frente a un agente quimioterapéutico, que comprende reducir la actividad, niveles de expresión o función de la ligasa de ubiquitina E3 Itch, usando ARNsi
6. Un método para identificar un agente que modula la actividad de la ligasa de ubiquitina E3 Itch, que comprende:
incubar un agente o agentes que se van a ensayar con una molécula de ligasa de ubiquitina E3 Itch en presencia de un sistema de ubiquitinación reconstituido in vitro,
determinar la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch en presencia del agente o agentes que se van a ensayar; y
seleccionar aquellos agentes que modulan la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch comparado con la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch en ausencia del agente o agentes que se van a ensayar,
comprendiendo además dicho método identificar aquellos agentes que modulan los niveles o actividad de p63 o p73.
7. Un método para identificar un agente que modula la actividad de la ligasa de ubiquitina E3 Itch, que comprende:
incubar un agente o agentes que se van a ensayar con una molécula de ligasa de ubiquitina E3 Itch en presencia de un sistema de ubiquitinación reconstituido in vitro,
determinar la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch en presencia del agente o agentes que se van a ensayar; y
seleccionar aquellos agentes que modulan la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch comparado con la cantidad de ubiquitina ligada a la ligasa de ubiquitina E3 Itch en ausencia del agente o agentes que se van a ensayar,
comprendiendo además dicho método identificar aquellos agentes que influyen en la unión de la ligasa de ubiquitina E3 Itch a p63 o p73.
8. Un método según cualquiera de las reivindicaciones 6 a 7, en donde el método es un ensayo ELISA.
9. Un método para identificar un agente que modula la actividad de la ligasa de ubiquitina E3 Itch, que comprende: incubar un agente o agentes que se van a ensayar con una molécula de ligasa de ubiquitina E3 Itch y una molécula ΔNp63, TAp73 o ΔNp73 en presencia de un sistema de ubiquitinación reconstituido in vitro,
determinar la presencia de formas ubiquitinadas de ΔNp63, TAp73 o ΔNp73 en presencia del agente o agentes que se van a ensayar; y
seleccionar aquellos agentes que modulan la cantidad de formas ubiquitinadas de ΔNp63, TAp73 o ΔNp73 comparado con la cantidad de dichas formas ubiquitinadas obtenidas en ausencia del agente o agentes que se van a ensayar.
10. Un método según cualquiera de las reivindicaciones 6 a 9, en donde el sistema de ubiquitinación comprende E1 y E2 en presencia de ATP.
11. Un método in vitro para identificar uno o más agentes capaces de modular la estabilidad de p63 o p73, que comprende las etapas de:
(a) incubar una molécula de ligasa de ubiquitina E3 Itch con el agente o agentes que se van a evaluar; y
(b) identificar estos agentes que influyen en la unión de la ligasa de ubiquitina E3 Itch a p63 o p73. 42
12. Un método para identificar un agente candidato para un producto farmacéutico útil en el tratamiento de una enfermedad, que comprende: incubar un agente o agentes que se van a ensayar con una molécula de ligasa de ubiquitina E3 Itch y una molécula ΔNp63, TAp73 o ΔNp73, en condiciones en las que, salvo por la presencia del agente o agentes que se van a ensayar, la ligasa de ubiquitina E3 Itch y ΔNp63, TAp73 o ΔNp73, forman un complejo con una afinidad de unión de referencia;
determinar la afinidad de unión del complejo de la ligasa de ubiquitina E3 Itch y ΔNp63, TAp73 o ΔNp73 en presencia del agente o agentes que se van a ensayar; y
seleccionar aquellos agentes que modulan la afinidad de unión del complejo con respecto a la afinidad de unión de referencia.
13. Uso de ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch para la fabricación de un medicamento para el tratamiento del cáncer, por administración simultánea o secuencial con un agente que daña el ADN.
14. ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch para usar en el tratamiento del cáncer.
15. Una combinación que comprende ARNsi o ARNsh para la ligasa de ubiquitina E3 Itch y un agente que daña el ADN, para usar en el tratamiento del cáncer.
16. Uso según la reivindicación 13, ARNsi según la reivindicación 14, o una combinación según la reivindicación 15, en donde dicho ARNsi comprende la secuencia AAGTGCTTCTCAGAATGATGA.
17. Uso según la reivindicación 13, ARNsi según la reivindicación 14, o una combinación según la reivindicación 15, en donde dicho ARNsi comprende la secuencia AACCACAACACACGAATTACA.
18. Un kit de diagnóstico que comprende el anticuerpo anti-ligasa de ubiquitina E3 Itch para usar en el diagnóstico 20 de tumores, midiendo la expresión de la ligasa de ubiquitina E3 Itch.
19. Un kit de diagnóstico que comprende cebador (es) para la detección de ARNm de la ligasa de ubiquitina E3 Itch, para usar en el diagnóstico de tumores, midiendo la expresión de la ligasa de ubiquitina E3 Itch.
Patentes similares o relacionadas:
 Composiciones y métodos para el tratamiento de trastornos de células plasmáticas y trastornos prolinfocíticos de células b, del 29 de Julio de 2020, de Knopp Biosciences LLC: Una composición que comprende una cantidad terapéuticamente eficaz de dexpramipexol para su uso en el tratamiento de un trastorno de células B caracterizado por niveles elevados […]
Composiciones y métodos para el tratamiento de trastornos de células plasmáticas y trastornos prolinfocíticos de células b, del 29 de Julio de 2020, de Knopp Biosciences LLC: Una composición que comprende una cantidad terapéuticamente eficaz de dexpramipexol para su uso en el tratamiento de un trastorno de células B caracterizado por niveles elevados […]
Derivados de piperidina 1,4 sustituidos, del 29 de Julio de 2020, de 89Bio Ltd: Un compuesto de acuerdo con la Fórmula I: **(Ver fórmula)** o una sal farmacéuticamente aceptable del mismo, en donde: A se selecciona de […]
Profármacos de gemcitabina, del 29 de Julio de 2020, de NuCana plc: Una formulación farmacéutica que comprende gemcitabina-[fenil-benzoxi-L-alaninil)]-(S)-fosfato 3: **(Ver fórmula)** o una sal o solvato […]
Formas cristalinas de 6-((6,7-dimetoxiquinazolin-4-il)oxi)-N,2-dimetilbenzofuran-3-carboxamida, del 29 de Julio de 2020, de Hutchison Medipharma Limited: Forma I de 6-((6,7-dimetoxiquinazolin-4-il)oxi)-N,2-dimetilbenzofuran-3-carboxamida, en donde el difractograma de rayos X de polvo de la Forma […]
Compuestos y procedimientos de uso, del 29 de Julio de 2020, de Medivation Technologies LLC: Un compuesto de fórmula (Aa-1): **(Ver fórmula)** o una sal farmacéuticamente aceptable del mismo, en la que: A representa H, halógeno, amino, […]
Complejos de agentes terapéuticos de base vírica y poli(beta-amino-ésteres) modificados, del 29 de Julio de 2020, de Sagetis Biotech, SL: Un complejo de un agente terapéutico de base vírica con un polímero de fórmula I: **(Ver fórmula)** donde cada L1 y L2 están seleccionados […]
Compuestos de alquinilbenceno heterocíclicos, y composiciones médicas y usos de los mismos, del 29 de Julio de 2020, de Guangzhou Healthquest Pharma Co., Ltd: Un compuesto de alquinilbenceno heterocíclico que tiene la fórmula (I) y una sal farmacéuticamente aceptable, o estereoisómero del mismo, **(Ver […]
Inmunoterapia novedosa contra diversos tumores, entre ellos tumores cerebrales y neuronales, del 22 de Julio de 2020, de IMMATICS BIOTECHNOLOGIES GMBH: Péptido que comprende una secuencia de aminoácidos acorde con la SEQ ID N.º 19, en que dicho péptido tiene una longitud total de entre 9 y 16 aminoácidos.