Método para la cuantificación absoluta de péptidos mediante espectrometría de masas en tándem, y sus usos.
Método para la cuantificación absoluta de péptidos mediante espectrometría de masas en tándem,
y sus usos utilizando péptidos enriquecidos isotópicamente en isótopos estables que presenten solapamiento espectral con el péptido de abundancia isotópica natural, monitorización de reacciones múltiples a baja resolución en el primer analizador de un espectrómetro de masas en tándem y regresión lineal múltiple. El método es también aplicable para la determinación indirecta de proteínas tras la hidrólisis de las proteínas con enzimas, la selección de uno o varios péptidos característicos de éstas y la determinación absoluta de estos péptidos. La invención resulta de aplicación en aquellos sectores en los que sea necesaria la cuantificación de proteínas y/o péptidos en una muestra, como puede ser en fluidos biológicos o en cultivos celulares, como por ejemplo en los sectores de la agricultura, la química, la farmacia, la biomedicina o la seguridad alimentaria.
Tipo: Patente de Invención. Resumen de patente/invención. Número de Solicitud: P201400239.
Solicitante: UNIVERSIDAD DE OVIEDO.
Nacionalidad solicitante: España.
Inventor/es: GARCIA ALONSO,JOSE IGNACIO, RODRIGUEZ GONZALEZ,Pablo, GONZALEZ ANTUÑA,Ana.
Fecha de Publicación: .
Clasificación Internacional de Patentes:
- G01N33/68 FISICA. › G01 METROLOGIA; ENSAYOS. › G01N INVESTIGACION O ANALISIS DE MATERIALES POR DETERMINACION DE SUS PROPIEDADES QUIMICAS O FISICAS (procedimientos de medida, de investigación o de análisis diferentes de los ensayos inmunológicos, en los que intervienen enzimas o microorganismos C12M, C12Q). › G01N 33/00 Investigación o análisis de materiales por métodos específicos no cubiertos por los grupos G01N 1/00 - G01N 31/00. › en los que intervienen proteínas, péptidos o aminoácidos.
PDF original: ES-2472724_A1.pdf




Fragmento de la descripción:
MÉTODO PARA LA CUANTIFICACIÓN ABSOLUTA DE PÉPTIDOS MEDIANTE ESPECTROMETRÃ?A DE MASAS EN TÃ?NDEM. Y SUS USOS
La presente invención se refiere a un método para la cuantificación absoluta de péptidos mediante espectrometría de masas en tándem utilizando péptidos enriquecidos isotópicamente con isótopos estables que presenten solapamiento espectral con el péptido de abundancia natural, monitorización de reacciones múltiples a baja resolución en el primer analizador y regresión lineal múltiple. El método es también aplicable para la determinación indirecta de proteínas tras su hidrólisis la selección de uno o varios péptidos característicos de éstas y la determinación absoluta de estos péptidos. La presente invención también se refiere a los usos del método para la cuantificación absoluta de péptidos.
La invención resulta de aplicación en aquellos sectores en los que sea necesaria la cuantificación de proteínas y/o péptidos en una muestra, como puede ser en fluidos biológicos o en cultivos celulares, como por ejemplo en los sectores de la agrícultura, la química, la fannacia, la biomedicina o la seguridad alimentaria.
ESTADO DE LA TÉCNICA
La expresión de los genes tiene Como resultado final la síntesis de péptidos y proteínas. Se considera que una cadena de aminoácidos es un péptido cuando contiene menos de 50 aminoácidos y que es una proteína cuando la cadena es más larga. En muestras biológicas se pueden encontrar tanto péptidos como proteínas. Estas biomoléculas son la llave para descifrar y entender la información contenida en el genoma de cualquier organismo vivo. El proteoma humano comprende más de 100.000 proteínas y péptidos con diferentes propiedades químicas que cubren concentraciones de hasta nueve órdenes de magnitud. Para llegar a entender moleculannente los procesos de las enfermedades es vital comparar sistemas celulares nonnales y en estado patológico para identificar y cuantificar los cambios que se efectúan en el proteoma. Esta tecnología se conoce con el nombre de proteómica cuantitativa y se basa en el análisis de proteínas y péptidos mediante distintas técnicas
--~---------~~--
incluyendo su marcaje metabólico, químico o enzimático. Los métodos analíticos desarrollados hasta la fecha en este campo están lejos de lograr la cuantificación de todas las proteínas y péptidos contenidos en un organismo. Sin embargo, la cromatografia líquida acoplada a la espectrometría de masas es una de las herramientas actuales más eficientes y prometedoras.
El uso de isótopos estables eruiquecidos juega un papel muy importante en el desarrollo de nuevas técnicas basadas en la cromatografia líquida acoplada a espectrometría de masas para la cuantificación de proteínas y péptidos ya que pennite el desarrollo de métodos de cuantifi<:ación mediante análisis por dilución isotópica (IDMS) . El análisis por dilución isotópica está considerado como un método absoluto de análisis que proporciona resultados directamente trazables al Sistema Internacional de unidades. Además, el uso de isótopos estables enriquecidos ha dado lugar al desarrollo de nuevas metodologías para explorar la dinámica de proteomas enteros y así proporcionar comparaciones relativas de las abundancias de las proteínas entre muestras (cuantificación relativa) , IDMS ha sido también empleado en el desarrollo de métodos capaces de proporcionar un alto nivel en la precisión y exactitud de la detenninación de proteínas (cuantificnción absoluta) .
La cuantificación relativa tü~ne como objetivo caracterizar cualitativa y cuantitativamente los cambios en la composición de un proteoma en función del genotipo, estado del ciclo celular, estado de la enfennedad y metabolismo de un fánnaco (Mosclcy A, "Current trends in differential expression proteomics: isolopically coded lags" Trends in Biotechnology 19 (2001) SIO) en lo que se ha venido llamando "expresión diferencial". Hay una gran cantidad de proteínas y péptidos que están involucrados en la respuesta a un estímulo, produciendo cambios en la señalización, transcripción, transducción y en las interacciones metabólicas de las modificaciones post-transduccionales. El reto reside en conocer los patrones de respuesta que se encuentran ocultos en ese cambio. El empleo de isótopos estables enriquecidos en combinación con la e:spectrometrfa de masas en tándem es una de las herramientas más eficaces para llevar a cabo el estudio de la expresión diferencial de las proteínas. Este tipo de cuantificación, conocida como cuantificación relativa, se basa en generar dos mezclas de proteoma: una isotópicamente emiquecida y otra con abundancia natural. La combinación de ambas mezclas durante la preparación de la muestra disminuye al mínimo las diferencias en la pérdida de proteínas o péptidos. Por tanto, la comparación de las intensidades de las señales correspondientes a cada mezcla de proteoma separadas por una diferencia de masa definida, proporcionará una medida en el nivel de la expresión relativa de los péptidos o proteínas en la muestra que se estudia (Bantscheff M, Schirle M, Sweetman G, Rick J, Kuster B "Quantitative mass spectrometr y in proteomics: a critical review" Anal.Bioanal. Chem. 389 (2007) 1017) . Es muy importante resaltar qut: este modo de cuantificación en ningún caso permite determinar la cantidad absoluta de proteína o péptido presente en una muestra. Los primeros procedimientos que se desarrollaron dentro de la cuantificación relativa con isótopos estables eruiquecidos fueron el marcaje metabólico (Y, Huang K, Cross F.R, Cowbum D, Chait B.T "Aecurate quantitation 01 protein expression and site-specijic phosphor y lation" Proc. Nattl. Acad. Sci. USA, 96 (1999) 6591; "Method lor the eomparative quantitative analysis 01 proteins and other biologieal material by isotopie labelling and mass spectrometr y " Pat. No. US 6, 391 , 649 Bl) y el marcaje estable de células en cultivo con aminoácidos enriquecidos isotópicamente, SILAC (Stable isotope labelling by aminoaeids in eell culture) (Ong S, Blagoev B, Kratchmarova 1, Kristensen D.B, Steen H, Pandey A, Mann M "Stable ¡sotope labeling by amino acids in cell culture, SILAC, as a simple and accurate approaeh to expression proteomics" Mol. CelL Proteomics 1 (2002) 376) . Posteriormente se desarrollaron métodos basados en el marcaje proteo lítico, como la introducción de la marca isotópica de forma simultánea con la digestión de la proteína ("Enzyme Catalyzed Isotope Labeling" Pat. No. US 2005/0032149; Fenselau C, Yao X ""O, -Labeling in Quantitative Proteomic Strategies: A Status Report" J. Proteome Res 8 (2009) 2140) . Sin embargo, los métodos más utilizados actualmente son los basados en el marcaje químico. Dependiendo del reactivo utilizado, se pueden encontrar numerosos métodos en la bibliografia (Julka S, Regnier F "Quantifieation in Proteomies through Stable ¡sotope Coding: A Review" J. Proteome Res 3 (2004) 350; I1iuk A, Galan J, Tao W.A "Playing tag with q:uantitative proteomics" Anal. Bioanal. Chem. 393 (2009) 503) . Por ejemplo, Goodl, , " y colaboradores (Goodlett D. R, Keller A,
Watts J.D, Newitt R, Yi E.C, Purvine S, Eng J.K, von Haller P, Aebersold R,
Kolker E "Diflerenttal stable isolope labeling ojpeptides for quanlitation and de
novosequence derivation" Rapid Commun. Mass Spectrom. 15 (2001) 1214)
propusieron en 2001 introducir pequeñas marcas después de la digestión triptica.
S Estas marcas consistían en utilizar akoholes deuterados para esterificar los grupos
carboxílicos de los péptidos (carboxilo tenninal y cadena lateral del ácido
glutámico y ácido aspártico) . Otro marcaje químico es conocido como "dimethyl
labelling" y consiste en utilizar fonnaldehído enriquecido con deuterio después de
la digestión (Hsu J, Huang S, Chow N, Chen S "Stable-tsotope dimethyl labeling
10 for quantilalive proteomics" Anal. Chem.75 (2003) 6843; "Reagen/ Kit ojGlobal
Analysis for Protein Expression and Melhod for Qualilalive and Quantitalive
Proteomic Analysis using the same" Patent No.: US 7, 338, 806 S2) . Gygi y
colaboradores (Gygi S. P, RiS! B, Gerber S.A, Turecek F, Gelb M.H, Aebersold R
"Quantitalive analysis of complex protein mixlures using isolope-coded affinity
15 lags" Nat. Siotechnol. 17 (1999) 994; "Rapid Quantitalive Analysis 01 Proleins or
Pro/ein Function in Complex Mixtures " Patent No.: US 6, 670, 194 SI)
desarrollaron otra estrategia de marcaje químico con isótopos estables y una
etiqueta de afinidad para la cuantificación relativa de proteínas en mezclas
complejas. En ella se procede a la dc:~rivatización química de los péptidos con un
20 reactivo conocido como ICAT. Este compuesto posee un extremo que... [Seguir leyendo]
Reivindicaciones:
l. Método para la cuantificación absoluta de péptidos en una muestra mediante espectrometría de masas en tándem que comprende los siguientes pasos:
a) selección de un péptido enriquecido isotópicamente, análogo químicamente al péptido a cuantificar, que presl~nte ~olapamiento espectral con el péptido de abundancia isotópica natural en UD espectro de masas;
b) selección de uno o varios iones precursores y de uno o varios iones producto que pennita la detección tanto del péptido de abundancia isotópica natural como del péptido enriquecido isotópicamente en un espectrómetro de masas en tándem;
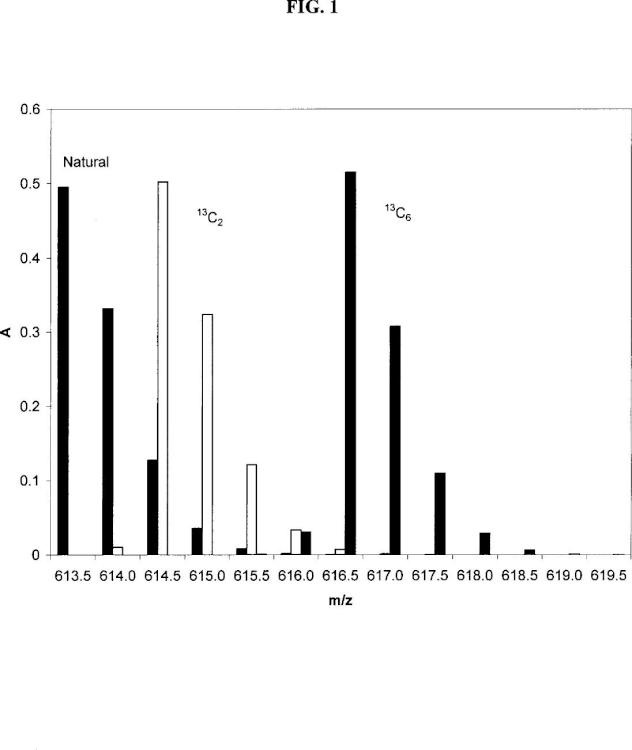
e) medida experimental de la composición isotópica del péptido de abundancia isotópica natural y del péptido enriquecido isotópicamente utilizando un espectrómetro de masas en tándem, ajustando la resolución en el primer analizador de masas de modo que el valor del FWHM esté entre 2 y 20 Y que la distribución isotópica medida (!n los iones producto seleccionados en b) se corresponda con las distribuciones isotópicas teóricas para los fragmentos tanto para el péptido de abundancia isotópica natural como para el enriquecido isotópicamente;
d) adición a la muestra de Wla cantidad conocida del péptido enriquecido isotópicamente seleccionado en a) ;
e) separación del péptido isotópicamente diluido de otros componentes de la muestra mediante cualquier técnica de separación fisica, química O bioquímica que separe el péptido isotópicamente diluido de sus interferentes;
f) medida de la distribución isotópica en iones fragmento del péptido isotópicamente diluido aislado en el paso e) utilizando el modo de medida optimizado en el paso e) en un espectrómetro de masas en tándem;
g) cálculo de las fracciones molares tanto del péptido de abundancia isotópica natural como del péptido enriquecido isotópicamente mediante regresión lineal
múltiple expresando la distribución isotópica obtenida experimentalmente en el paso f) como una combinación lineal de las composiciones isotópicas del péptido de abundancia isotópica natural y del péptido enriquecido isotópicamente medidas en el paso c) ;
s h) cálculo del número de moles del péptido de abundancia isotópica natural a partir de la relación de las fracciones molares detenninadas en el paso g) y del número de moles conocido del péptido enriquecido isotópicamente añadidos a la muestra en el paso d) .
10 2. Método según la reivindicación 1 caracterizado por que la muestra es un fluido biológico, un cultivo celular o cualquier otra muestra biológica que contenga péptidos o proteínas.
3. Método según la reivindicación 2 caracterizado por que además comprende un paso de hidrólisis de la muestm para romper las proteínas y liberar sus péptidos constituyentes, previo al paso d) .
15 4. Método según la reivindicación 2 caracterizado por que además comprende un paso de hidrólisis de la muestra para romper las proteínas y liberar sus péptidos constituyentes, posterior al paso d) .
20 5. Método según la reivindicación 2 caracterizado por que además comprende un paso de hidrólisis de la muestra p::tra romper las proteínas y liberar sus péptidos constituyentes, posterior al paso e) .
6. Método según las reivindicaciones 3, 4 ó 5 caracterizado por que la hidrólisis es enzimática y el péptido constituyente a cuantificar es característico de la proteína.
25 7. Método según la reivindicación I caracterizado por que el péptido enriquecido isotópicamente contiene entre 1 y 4-átomos de alguno de los isótopos enriquecidos I3C ' ¡SN l' b'"o en cua qUler com maClOn.
8. Método según la reivindicación l caracterizado por que el péptido enriquecido isotópicamente se sintetiza químic:amente utilizando distintas combinaciones de , "d ' 'd IJC ' ¡SN amInOaCl os ennquecl os en o .
9. Método según la reivindicación l caracterizado por que el ión precursor seleccionado en el paso b) posee carga +2 ó +3 y el ión producto seleccionado posee carga +l.
10. Método según la reivindicación 1 caracterizado por que el espectrómetro de masas en tándem es de tipo triple cuadrupolo.
11. Método según la reivindicación 10 caracterizado por que el espectrómetro de masas en tándem de tipo triple cuadrupolo es con trampa lineal en el tercer cuadrupolo.
12. Método según la reivindicación 1 caracterizado por que el espectrómetro de masas en tándem es un equipo de ti:po cuadrupolo-tiempo de vuelo (Q-TOF) .
13. Método según la reivindicación 1 caracterizado por que en el paso c) además se reduce el FWHM en el tercer cuadrupolo a un valor entre 0.7 y OA, hasta comprobar que la distribución :isotópica medida en los iones producto se corresponde con las distribuciones isotópicas teóricas calculadas para los fmgmentos tanto para el péptido natural como para el enriquecido isotópicamente.
14. Método según la reivindicación 1 caracterizado por que el método fisico para la separación en la etapa e) del péptido isotópicamente diluido del resto de la muestra es la centrifugación.
15. Método según la reivindicación I caracterizado por que el método químico para la separación en la etapa e) del péptido isotópicamente diluido del resto de la muestra es la cromatografia de intercambio jónico, reparto o afinidad.
16. Método según la reivindicación I caracterizado por que la separación del péptido isotópicamente diluido del resto de la muestra se realiza por cromatografia liquida acoplada al espectrómetro de masas en tándem.
17. Método según la reivindicación 16 caracterizado por que la medida de las abundancias isotópicas en el espectrómetro de masas en tándem de los pasos c) y f) se realiza a partir de las áreas de pico obtenidas para el péptido isotópicamente diluido tras la separación cromatográfica.
18. Método según la reivindicación I caracterizado por que el método bioquímico para la separación en la etapa e) de:l péptido isotópicamente diluido del resto de la muestra es la irununoprecipitación.
19. Método según la reivindicación l caracterizado por que en el paso f) se mide un
mínimo de 2 y un máximo de 6 transiciones para cada combinación ión precursor ión producto seleccionado.
20. Método según la reivindicación 1 caracterizado por que las abundancias isotópicas para el péptido de abundancia isotópica natural y el enriquecido isotópicamente medidas en el paso c) y utilizadas en la regresión lineal múltiple del
paso g) se determinan matemáticarnente mediante un programa de ordenador.
21. Uso del método según las reivindicaciones 1 a 20 como herramienta de diagnóstico clínico.
22. Uso del método según las reivi.ndicaciones 1 a 20 para el análisis de muestras de alimentos y la certificación de su seguridad alimentaria.
1S 23. Uso del método según las reivindicaciones 1 a 20 como herramienta para el análisis de muestras fannacéuticas.
24. Uso del método según las reivindicaciones l a 20 para el análisis de muestras en biomedicina.
25. Uso del método según las reivindicaciones 1 a 20 para el análisis de muestras 20 en metrología química.
Patentes similares o relacionadas:
Inmunomoduladores, del 29 de Julio de 2020, de BRISTOL-MYERS SQUIBB COMPANY: Un compuesto de la fórmula (I) **(Ver fórmula)** o una sal farmacéuticamente aceptable del mismo, en donde: A se selecciona de **(Ver fórmula)** en donde: […]
Métodos y composiciones para el diagnóstico y pronóstico de lesión renal e insuficiencia renal, del 29 de Julio de 2020, de Astute Medical, Inc: Un método para evaluar el estado renal en un sujeto, que comprende: realizar una pluralidad de ensayos configurados para detectar una […]
Neuregulina para tratar la insuficiencia cardíaca, del 29 de Julio de 2020, de Zensun (Shanghai) Science & Technology, Co., Ltd: Neuregulina para usar en un método para tratar la insuficiencia cardíaca crónica en un paciente, donde el paciente tiene un nivel plasmático de NT-proBNP […]
Método para llevar a cabo el seguimiento de la enfermedad de Gaucher, del 15 de Julio de 2020, de Centogene GmbH: Un método para determinar la evolución de la enfermedad de Gaucher en un sujeto, que comprende la etapa de determinar en varios puntos en el […]
Procedimiento para evaluación de la función hepática y el flujo sanguíneo portal, del 15 de Julio de 2020, de The Regents of the University of Colorado, a body corporate: Procedimiento in vitro para la estimación del flujo sanguíneo portal en un individuo a partir de una única muestra de sangre o suero, comprendiendo el procedimiento: […]
Detección de interacciones proteína a proteína, del 15 de Julio de 2020, de THE GOVERNING COUNCIL OF THE UNIVERSITY OF TORONTO: Un método para medir cuantitativamente la fuerza y la afinidad de una interacción entre una primera proteína de membrana o parte de la misma y una […]
Biomarcadores de pronóstico y predictivos y aplicaciones biológicas de los mismos, del 1 de Julio de 2020, de INSTITUT GUSTAVE ROUSSY: Un método para evaluar la sensibilidad o la resistencia de un tumor frente a un agente antitumoral, que comprende evaluar la cantidad de complejo eiF4E-eiF4G (complejo Cap-ON) […]
Métodos de monitorización terapéutica de profármacos de ácido fenilacético, del 24 de Junio de 2020, de Immedica Pharma AB: Glicerilo tri-[4-fenilbutirato] (HPN-100) para su uso en un método para tratar un trastorno del ciclo de la urea en un sujeto que tiene discapacidad […]